이 번역 페이지는 최신 내용을 담고 있지 않습니다. 최신 내용을 영문으로 보려면 여기를 클릭하십시오.
anovan
다원분산분석
구문
설명
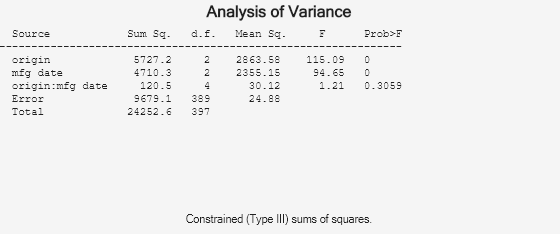
p = anovan(y,group,Name,Value)Name,Value 쌍 인수로 지정된 추가 옵션을 사용하여 다원분산분석(n-way ANOVA)에 대한 p-값으로 구성된 벡터를 반환합니다.
예를 들어, 어떤 예측 변수가 연속형 예측 변수인지 여부, 또는 사용할 제곱합 유형을 지정할 수 있습니다.
[은 어떤 그룹 평균의 쌍이 현저히 다른지 판별할 수 있게 해주는 다중 비교 검정을 수행하는 데 사용할 수 있는 p,tbl,stats] = anovan(___)stats 구조체를 반환합니다. stats 구조체를 입력값으로 하여 multcompare 함수를 사용하여 이러한 검정을 수행할 수 있습니다.
예제
입력 인수
이름-값 인수
출력 인수
대체 기능
anovan 함수를 사용하는 대신에, anova 함수를 사용하여 anova 객체를 만들 수 있습니다. anova 함수는 다음과 같은 이점을 제공합니다.
anova함수를 사용하면 분산분석 모델 유형, 제곱합 유형, 범주형으로 처리할 인자를 지정할 수 있습니다.anova는 또한 table형 예측 변수와 응답 변수를 입력 인수로 사용할 수 있습니다.anovan에서 반환하는 출력값 외에,anova객체의 속성에는 다음이 포함됩니다.분산분석 모델식
피팅된 분산분석 모델 계수
잔차
인자와 응답 변수 데이터
anova객체 함수를 사용하면anova객체를 피팅한 후 추가 분석을 수행할 수 있습니다. 예를 들어 분산분석을 위해 평균에 대한 다중 비교를 대화형 플롯으로 만들고, 인자의 각 값에 대해 평균 응답 변수의 추정값을 구하고, 분산 성분 추정값을 계산할 수 있습니다.
참고 문헌
[1] Dunn, O.J., and V.A. Clark. Applied Statistics: Analysis of Variance and Regression. New York: Wiley, 1974.
[2] Goodnight, J.H., and F.M. Speed. Computing Expected Mean Squares. Cary, NC: SAS Institute, 1978.
[3] Seber, G. A. F., and A. J. Lee. Linear Regression Analysis. 2nd ed. Hoboken, NJ: Wiley-Interscience, 2003.
버전 내역
R2006a 이전에 개발됨