이 번역 페이지는 최신 내용을 담고 있지 않습니다. 최신 내용을 영문으로 보려면 여기를 클릭하십시오.
fitrgp
가우스 과정 회귀(GPR) 모델 피팅
구문
설명
Mdl = fitrgp(Tbl,ResponseVarName)Tbl에 포함된 표본 데이터를 사용하여 훈련된 가우스 과정 회귀(GPR) 모델을 반환합니다. 여기서 ResponseVarName은 Tbl에 포함된 응답 변수의 이름입니다.
Mdl = fitrgp(___,Name,Value)Name,Value 쌍의 인수로 지정된 추가 옵션을 사용하여 위에 열거된 구문에 나와 있는 입력 인수에 대한 GPR 모델을 반환합니다.
예를 들어, 피팅 방법, 예측 방법, 공분산 함수 또는 활성 세트 선택 방법을 지정할 수 있습니다. 교차 검증된 모델을 훈련시킬 수도 있습니다.
Mdl은 RegressionGP 객체입니다. 이 객체의 객체 함수와 속성은 RegressionGP를 참조하십시오.
교차 검증된 모델을 훈련시키는 경우 Mdl은 RegressionPartitionedGP 객체입니다. 교차 검증된 객체에 대한 추가 분석을 수행하려면 RegressionPartitionedGP 객체의 객체 함수를 사용하십시오.
[는 사용자가 Mdl,AggregateOptimizationResults] = fitrgp(___)OptimizeHyperparameters와 HyperparameterOptimizationOptions 이름-값 인수를 지정하는 경우 하이퍼파라미터 최적화 결과를 포함하는 AggregateOptimizationResults도 반환합니다. HyperparameterOptimizationOptions의 ConstraintType 옵션과 ConstraintBounds 옵션도 지정해야 합니다. 이 구문을 사용하면 교차 검증 손실 대신에 간소 모델 크기에 대해 최적화하고, 옵션은 동일하지만 제약 조건 범위가 다른 여러 최적화 문제 세트를 수행할 수 있습니다.
예제
이 예제에서는 UCI Machine Learning Repository [3]의 전복 데이터 [1], [2]를 사용합니다. 데이터를 다운로드한 후 abalone.data라는 이름으로 현재 폴더에 저장합니다.
데이터를 테이블에 저장합니다. 처음 7개 행을 표시합니다.
tbl = readtable('abalone.data','Filetype','text',... 'ReadVariableNames',false); tbl.Properties.VariableNames = {'Sex','Length','Diameter','Height',... 'WWeight','SWeight','VWeight','ShWeight','NoShellRings'}; tbl(1:7,:)
ans =
Sex Length Diameter Height WWeight SWeight VWeight ShWeight NoShellRings
___ ______ ________ ______ _______ _______ _______ ________ ____________
'M' 0.455 0.365 0.095 0.514 0.2245 0.101 0.15 15
'M' 0.35 0.265 0.09 0.2255 0.0995 0.0485 0.07 7
'F' 0.53 0.42 0.135 0.677 0.2565 0.1415 0.21 9
'M' 0.44 0.365 0.125 0.516 0.2155 0.114 0.155 10
'I' 0.33 0.255 0.08 0.205 0.0895 0.0395 0.055 7
'I' 0.425 0.3 0.095 0.3515 0.141 0.0775 0.12 8
'F' 0.53 0.415 0.15 0.7775 0.237 0.1415 0.33 20데이터셋에는 4177개의 관측값이 있습니다. 8개 물리적 측정값에서 전복의 나이를 예측하는 것이 목적입니다. 마지막 변수인 껍데기의 나이테 수가 전복의 나이입니다. 첫 번째 예측 변수는 범주형 변수입니다. 테이블의 마지막 변수는 응답 변수입니다.
모수 추정에 부분 회귀 변수 방법을 사용하고 예측에 완전히 독립적인 조건부 방법을 사용하여 GPR 모델을 피팅합니다. 예측 변수를 표준화합니다.
gprMdl = fitrgp(tbl,'NoShellRings','KernelFunction','ardsquaredexponential',... 'FitMethod','sr','PredictMethod','fic','Standardize',1)
grMdl =
RegressionGP
PredictorNames: {1x8 cell}
ResponseName: 'Var9'
ResponseTransform: 'none'
NumObservations: 4177
KernelFunction: 'ARDSquaredExponential'
KernelInformation: [1x1 struct]
BasisFunction: 'Constant'
Beta: 10.9148
Sigma: 2.0243
PredictorLocation: [10x1 double]
PredictorScale: [10x1 double]
Alpha: [1000x1 double]
ActiveSetVectors: [1000x10 double]
PredictMethod: 'FIC'
ActiveSetSize: 1000
FitMethod: 'SR'
ActiveSetMethod: 'Random'
IsActiveSetVector: [4177x1 logical]
LogLikelihood: -9.0013e+03
ActiveSetHistory: [1x1 struct]
BCDInformation: []
훈련된 모델을 사용하여 응답 변수를 예측합니다.
ypred = resubPredict(gprMdl);
실제 응답과 예측된 응답을 플로팅합니다.
figure(); plot(tbl.NoShellRings,'r.'); hold on plot(ypred,'b'); xlabel('x'); ylabel('y'); legend({'data','predictions'},'Location','Best'); axis([0 4300 0 30]); hold off;

훈련된 모델에 대한 훈련 데이터의 회귀 손실(재대입 손실)을 계산합니다.
L = resubLoss(gprMdl)
L =
4.0064표본 데이터를 생성합니다.
rng(0,'twister'); % For reproducibility n = 1000; x = linspace(-10,10,n)'; y = 1 + x*5e-2 + sin(x)./x + 0.2*randn(n,1);
모수를 추정하기 위해 선형 기저 함수와 정확한 피팅 방법을 사용하여 GPR 모델을 피팅합니다. 또한 정확한 예측 방법도 사용합니다.
gprMdl = fitrgp(x,y,'Basis','linear',... 'FitMethod','exact','PredictMethod','exact');
훈련된 모델을 사용하여 x(재대입 예측값)의 행에 대응되는 응답 변수를 예측합니다.
ypred = resubPredict(gprMdl);
응답 변수의 실제 값을 예측 값과 함께 플로팅합니다.
plot(x,y,'b.'); hold on; plot(x,ypred,'r','LineWidth',1.5); xlabel('x'); ylabel('y'); legend('Data','GPR predictions'); hold off
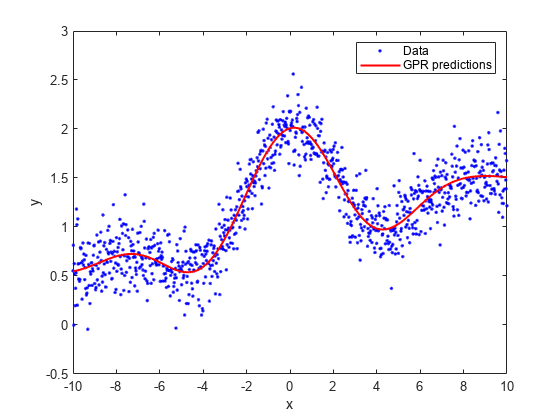
표본 데이터를 불러옵니다.
load('gprdata2.mat')이 데이터에는 하나의 예측 변수와 연속형 응답 변수가 있습니다. 이는 시뮬레이션된 데이터입니다.
디폴트 커널 모수를 갖는 제곱 지수 커널 함수를 사용하여 GPR 모델을 피팅합니다.
gprMdl1 = fitrgp(x,y,'KernelFunction','squaredexponential');
이제, 두 번째 모델을 피팅합니다. 여기서는 커널 모수의 초기값을 지정합니다.
sigma0 = 0.2; kparams0 = [3.5, 6.2]; gprMdl2 = fitrgp(x,y,'KernelFunction','squaredexponential',... 'KernelParameters',kparams0,'Sigma',sigma0);
두 모델 모두에서 재대입 예측값을 계산합니다.
ypred1 = resubPredict(gprMdl1); ypred2 = resubPredict(gprMdl2);
두 모델 모두에서 계산한 응답 변수 예측값과 훈련 데이터의 응답 변수 값을 플로팅합니다.
figure(); plot(x,y,'r.'); hold on plot(x,ypred1,'b'); plot(x,ypred2,'g'); xlabel('x'); ylabel('y'); legend({'data','default kernel parameters',... 'kparams0 = [3.5,6.2], sigma0 = 0.2'},... 'Location','Best'); title('Impact of initial kernel parameter values'); hold off
![Figure contains an axes object. The axes object with title Impact of initial kernel parameter values, xlabel x, ylabel y contains 3 objects of type line. One or more of the lines displays its values using only markers These objects represent data, default kernel parameters, kparams0 = [3.5,6.2], sigma0 = 0.2.](impactofspecifyinginitialkernelparametervaluesexample_01_ko_KR.png)
fitrgp가 GPR 모수를 추정하기 위해 최대화하는 주변 로그 가능도에 여러 국소해가 있으며, 수렴되는 해는 초기점에 따라 달라집니다. 각 국소해는 특정한 데이터 해석 방식에 대응합니다. 이 예제에서 디폴트 초기 커널 모수를 갖는 해는 잡음이 높은 저주파 신호에 해당하는 반면, 사용자 지정 초기 커널 모수를 갖는 두 번째 해는 잡음이 낮은 고주파 신호에 해당합니다.
표본 데이터를 불러옵니다.
load('gprdata.mat')6개의 연속형 예측 변수가 있습니다. 훈련 데이터 세트에는 500개의 관측값이 있고 테스트 데이터 세트에는 100개의 관측값이 있습니다. 이는 시뮬레이션된 데이터입니다.
각 예측 변수마다 개별적인 길이 스케일을 갖는 제곱 지수 커널 함수를 사용하여 GPR 모델을 피팅합니다. 이 공분산 함수는 다음과 같이 정의됩니다.
여기서 은 예측 변수 ( = 1, 2, ..., )에 대한 길이 스케일을 나타내고 는 신호 표준편차입니다. 비제약 모수화 는 다음과 같습니다.
커널 함수의 길이 스케일을 10으로 초기화하고 신호 표준편차와 잡음 표준편차를 응답 변수의 표준편차로 초기화합니다.
sigma0 = std(ytrain); sigmaF0 = sigma0; d = size(Xtrain,2); sigmaM0 = 10*ones(d,1);
초기 커널 모수 값을 사용하여 GPR 모델을 피팅합니다. 훈련 데이터에서 예측 변수를 표준화합니다. 정확한 피팅 방법과 예측 방법을 사용합니다.
gprMdl = fitrgp(Xtrain,ytrain,'Basis','constant','FitMethod','exact',... 'PredictMethod','exact','KernelFunction','ardsquaredexponential',... 'KernelParameters',[sigmaM0;sigmaF0],'Sigma',sigma0,'Standardize',1);
검정 데이터에 대해 회귀 손실을 계산합니다.
L = loss(gprMdl,Xtest,ytest)
L = 0.6919
커널 정보에 액세스합니다.
gprMdl.KernelInformation
ans = struct with fields:
Name: 'ARDSquaredExponential'
KernelParameters: [7×1 double]
KernelParameterNames: {7×1 cell}
커널 모수 이름을 표시합니다.
gprMdl.KernelInformation.KernelParameterNames
ans = 7×1 cell
{'LengthScale1'}
{'LengthScale2'}
{'LengthScale3'}
{'LengthScale4'}
{'LengthScale5'}
{'LengthScale6'}
{'SigmaF' }
커널 모수를 표시합니다.
sigmaM = gprMdl.KernelInformation.KernelParameters(1:end-1,1)
sigmaM = 6×1
104 ×
0.0004
0.0007
0.0004
4.7665
0.1018
0.0056
sigmaF = gprMdl.KernelInformation.KernelParameters(end)
sigmaF = 28.1720
sigma = gprMdl.Sigma
sigma = 0.8162
학습된 길이 스케일의 로그를 플로팅합니다.
figure() plot((1:d)',log(sigmaM),'ro-'); xlabel('Length scale number'); ylabel('Log of length scale');

4번째 및 5번째 예측 변수에 대한 길이 스케일의 로그는 다른 변수보다 상대적으로 높습니다. 이러한 예측 변수는 다른 예측 변수만큼 응답 변수에 미치는 영향이 크지 않은 것으로 보입니다.
4번째 및 5번째 변수를 예측 변수로 사용하지 않고 GPR 모델을 피팅합니다.
X = [Xtrain(:,1:3) Xtrain(:,6)]; sigma0 = std(ytrain); sigmaF0 = sigma0; d = size(X,2); sigmaM0 = 10*ones(d,1); gprMdl = fitrgp(X,ytrain,'Basis','constant','FitMethod','exact',... 'PredictMethod','exact','KernelFunction','ardsquaredexponential',... 'KernelParameters',[sigmaM0;sigmaF0],'Sigma',sigma0,'Standardize',1);
검정 데이터에 대한 회귀 오차를 계산합니다.
xtest = [Xtest(:,1:3) Xtest(:,6)]; L = loss(gprMdl,xtest,ytest)
L = 0.6928
손실은 모든 변수가 예측 변수로 사용된 경우의 손실과 유사합니다.
검정 데이터에 대해 예측된 응답 값을 계산합니다.
ypred = predict(gprMdl,xtest);
피팅된 값과 함께 원래 응답 변수 값을 플로팅합니다.
figure; plot(ytest,'r'); hold on; plot(ypred,'b'); legend('True response','GPR predicted values','Location','Best'); hold off

이 예제에서는 fitrgp를 사용하여 자동으로 하이퍼파라미터를 최적화하는 방법을 보여줍니다. 이 예제에서는 소프트웨어와 함께 제공되는 gprdata2 데이터를 사용합니다.
데이터를 불러옵니다.
load('gprdata2.mat')이 데이터에는 하나의 예측 변수와 연속형 응답 변수가 있습니다. 이는 시뮬레이션된 데이터입니다.
디폴트 커널 모수를 갖는 제곱 지수 커널 함수를 사용하여 GPR 모델을 피팅합니다.
gprMdl1 = fitrgp(x,y,'KernelFunction','squaredexponential');
자동 하이퍼파라미터 최적화를 사용하여 5겹 교차 검증 손실을 최소화하는 하이퍼파라미터를 구합니다.
재현이 가능하도록 난수 시드값을 설정하고 'expected-improvement-plus' 획득 함수를 사용합니다.
rng default gprMdl2 = fitrgp(x,y,'KernelFunction','squaredexponential',... 'OptimizeHyperparameters','auto','HyperparameterOptimizationOptions',... struct('AcquisitionFunctionName','expected-improvement-plus'));
|=====================================================================================================|
| Iter | Eval | Objective: | Objective | BestSoFar | BestSoFar | Sigma | Standardize |
| | result | log(1+loss) | runtime | (observed) | (estim.) | | |
|=====================================================================================================|
| 1 | Best | 0.42258 | 1.1605 | 0.42258 | 0.42258 | 2.7255 | false |
| 2 | Accept | 1.1091 | 1.2987 | 0.42258 | 0.61465 | 0.0057724 | true |
| 3 | Accept | 1.6498 | 0.64246 | 0.42258 | 0.75989 | 25.905 | true |
| 4 | Best | 0.29824 | 1.1509 | 0.29824 | 0.29834 | 0.0098001 | false |
| 5 | Accept | 1.0387 | 1.2971 | 0.29824 | 0.49293 | 0.00010004 | false |
| 6 | Best | 0.037911 | 0.89251 | 0.037911 | 0.038158 | 0.13791 | false |
| 7 | Accept | 0.042394 | 0.89713 | 0.037911 | 0.038142 | 0.079273 | false |
| 8 | Accept | 0.038899 | 1.0254 | 0.037911 | 0.037126 | 0.11545 | false |
| 9 | Accept | 0.038969 | 0.94532 | 0.037911 | 0.037592 | 0.11307 | false |
| 10 | Accept | 0.039193 | 0.93499 | 0.037911 | 0.037928 | 0.1124 | false |
| 11 | Accept | 1.1496 | 1.192 | 0.037911 | 0.03793 | 0.0001 | true |
| 12 | Accept | 0.13152 | 0.90279 | 0.037911 | 0.038375 | 0.37155 | true |
| 13 | Accept | 0.037915 | 0.89099 | 0.037911 | 0.038351 | 0.13701 | true |
| 14 | Best | 0.037785 | 0.85139 | 0.037785 | 0.038272 | 0.18141 | true |
| 15 | Best | 0.037697 | 0.99207 | 0.037697 | 0.03876 | 0.32603 | false |
| 16 | Accept | 0.037716 | 1.2438 | 0.037697 | 0.038783 | 0.22469 | false |
| 17 | Accept | 0.037832 | 0.97469 | 0.037697 | 0.036007 | 0.16182 | true |
| 18 | Accept | 0.037702 | 0.9163 | 0.037697 | 0.036011 | 0.23962 | false |
| 19 | Accept | 0.037838 | 1.3736 | 0.037697 | 0.036467 | 0.15992 | true |
| 20 | Best | 0.037694 | 1.1649 | 0.037694 | 0.036469 | 0.24919 | false |
|=====================================================================================================|
| Iter | Eval | Objective: | Objective | BestSoFar | BestSoFar | Sigma | Standardize |
| | result | log(1+loss) | runtime | (observed) | (estim.) | | |
|=====================================================================================================|
| 21 | Accept | 0.037841 | 1.0979 | 0.037694 | 0.03675 | 0.15878 | true |
| 22 | Accept | 0.037765 | 1.0761 | 0.037694 | 0.036751 | 0.19128 | false |
| 23 | Best | 0.037683 | 0.91286 | 0.037683 | 0.036752 | 0.27578 | false |
| 24 | Accept | 2.1082 | 0.84632 | 0.037683 | 0.036754 | 29.263 | false |
| 25 | Accept | 0.42164 | 0.74832 | 0.037683 | 0.034063 | 0.5675 | false |
| 26 | Accept | 0.29404 | 0.98572 | 0.037683 | 0.034072 | 0.029617 | false |
| 27 | Accept | 1.0384 | 0.90096 | 0.037683 | 0.034106 | 0.0021049 | false |
| 28 | Accept | 0.28288 | 1.1858 | 0.037683 | 0.034043 | 0.051917 | true |
| 29 | Accept | 0.42298 | 0.78889 | 0.037683 | 0.03404 | 1.3844 | true |
| 30 | Accept | 0.29873 | 1.5461 | 0.037683 | 0.034238 | 0.00073587 | true |
__________________________________________________________
Optimization completed.
MaxObjectiveEvaluations of 30 reached.
Total function evaluations: 30
Total elapsed time: 46.9732 seconds
Total objective function evaluation time: 30.8366
Best observed feasible point:
Sigma Standardize
_______ ___________
0.27578 false
Observed objective function value = 0.037683
Estimated objective function value = 0.034238
Function evaluation time = 0.91286
Best estimated feasible point (according to models):
Sigma Standardize
_______ ___________
0.27578 false
Estimated objective function value = 0.034238
Estimated function evaluation time = 0.98076


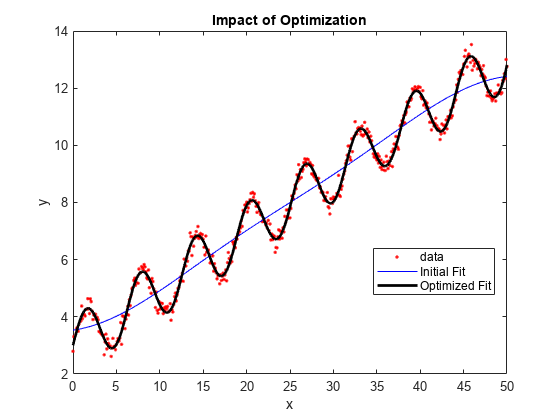
최적화 전 피팅과 최적화 후 피팅을 비교합니다.
ypred1 = resubPredict(gprMdl1); ypred2 = resubPredict(gprMdl2); figure(); plot(x,y,'r.'); hold on plot(x,ypred1,'b'); plot(x,ypred2,'k','LineWidth',2); xlabel('x'); ylabel('y'); legend({'data','Initial Fit','Optimized Fit'},'Location','Best'); title('Impact of Optimization'); hold off
이 예제에서는 UCI Machine Learning Repository [3]의 전복 데이터 [1], [2]를 사용합니다. 데이터를 다운로드한 후 abalone.data라는 이름으로 현재 폴더에 저장합니다.
데이터를 table로 저장합니다. 처음 7개 행을 표시합니다.
tbl = readtable('abalone.data','Filetype','text','ReadVariableNames',false); tbl.Properties.VariableNames = {'Sex','Length','Diameter','Height','WWeight','SWeight','VWeight','ShWeight','NoShellRings'}; tbl(1:7,:)
ans =
Sex Length Diameter Height WWeight SWeight VWeight ShWeight NoShellRings
___ ______ ________ ______ _______ _______ _______ ________ ____________
'M' 0.455 0.365 0.095 0.514 0.2245 0.101 0.15 15
'M' 0.35 0.265 0.09 0.2255 0.0995 0.0485 0.07 7
'F' 0.53 0.42 0.135 0.677 0.2565 0.1415 0.21 9
'M' 0.44 0.365 0.125 0.516 0.2155 0.114 0.155 10
'I' 0.33 0.255 0.08 0.205 0.0895 0.0395 0.055 7
'I' 0.425 0.3 0.095 0.3515 0.141 0.0775 0.12 8
'F' 0.53 0.415 0.15 0.7775 0.237 0.1415 0.33 20데이터셋에는 4177개의 관측값이 있습니다. 8개 물리적 측정값에서 전복의 나이를 예측하는 것이 목적입니다. 마지막 변수인 껍데기의 나이테 수가 전복의 나이입니다. 첫 번째 예측 변수는 범주형 변수입니다. 테이블의 마지막 변수는 응답 변수입니다.
검증에 데이터의 25%를 사용하여 교차 검증된 GPR 모델을 훈련시킵니다.
rng('default') % For reproducibility cvgprMdl = fitrgp(tbl,'NoShellRings','Standardize',1,'Holdout',0.25);
겹 바깥의 관측값에 대해 훈련된 모델을 사용하여 겹에 대한 평균 손실을 계산합니다.
kfoldLoss(cvgprMdl)
ans = 4.6409
겹 바깥의 데이터에 대한 응답 변수를 예측합니다.
ypred = kfoldPredict(cvgprMdl);
검정에 사용되는 실제 응답 변수 값과 예측 값을 플로팅합니다.
figure(); plot(ypred(cvgprMdl.Partition.test)); hold on; y = table2array(tbl(:,end)); plot(y(cvgprMdl.Partition.test),'r.'); axis([0 1050 0 30]); xlabel('x') ylabel('y') hold off;

표본 데이터를 생성합니다.
rng(0,'twister'); % For reproducibility n = 1000; x = linspace(-10,10,n)'; y = 1 + x*5e-2 + sin(x)./x + 0.2*randn(n,1);
제곱 지수 커널 함수를 사용자 지정 커널 함수로 정의합니다.
제곱 지수 커널 함수를 다음과 같이 계산할 수 있습니다.
여기서 는 신호 표준편차이고, 은 길이 스케일입니다. 및 은 모두 0보다 커야 합니다. 이 조건은 일부 비제약 모수화 벡터 에서 비제약 모수화 및 로 강제될 수 있습니다.
따라서 다음과 같이 제곱 지수 커널 함수를 사용자 지정 커널 함수로 정의할 수 있습니다.
kfcn = @(XN,XM,theta) (exp(theta(2))^2)*exp(-(pdist2(XN,XM).^2)/(2*exp(theta(1))^2));
여기서 pdist2(XN,XM).^2은 거리 행렬을 계산합니다.
사용자 지정 커널 함수 kfcn을 사용하여 GPR 모델을 피팅합니다. 커널 모수의 초기값을 지정합니다(사용자 지정 커널 함수를 사용하고 있으므로 비제약 모수화 벡터 theta의 초기값을 지정해야 함).
theta0 = [1.5,0.2]; gprMdl = fitrgp(x,y,'KernelFunction',kfcn,'KernelParameters',theta0);
fitrgp는 내장 커널 함수를 사용할 때 해석적 도함수를 사용하여 모수를 추정하는 반면, 사용자 지정 커널 함수를 사용할 때는 수치적 도함수를 사용합니다.
이 모델에 대한 재대입 손실을 계산합니다.
L = resubLoss(gprMdl)
L = 0.0391
내장 제곱 지수 커널 함수 옵션을 사용하여 GPR 모델을 피팅합니다. 커널 모수의 초기값을 지정합니다(내장 사용자 지정 커널 함수를 사용하고 초기 모수 값을 지정하는 중이므로 신호 표준편차와 길이 스케일의 초기값을 직접 지정해야 함).
sigmaL0 = exp(1.5); sigmaF0 = exp(0.2); gprMdl2 = fitrgp(x,y,'KernelFunction','squaredexponential','KernelParameters',[sigmaL0,sigmaF0]);
이 모델에 대한 재대입 손실을 계산합니다.
L2 = resubLoss(gprMdl2)
L2 = 0.0391
예상대로 두 손실 값이 같습니다.
다수의 예측 변수를 사용하여 생성된 데이터에 대해 GPR 모델을 훈련시킵니다. LBFGS 최적화 함수에 대한 초기 스텝 크기를 지정합니다.
결과 재현이 가능하도록 난수 생성기의 유형과 시드값을 설정합니다.
rng(0,'twister'); % For reproducibility
300개의 관측값과 3000개의 예측 변수로 구성된 표본 데이터를 생성합니다. 여기서 응답 변수는 4번째, 7번째, 13번째 예측 변수에 따라 결정됩니다.
N = 300; P = 3000; X = rand(N,P); y = cos(X(:,7)) + sin(X(:,4).*X(:,13)) + 0.1*randn(N,1);
커널 모수의 초기값을 설정합니다.
sigmaL0 = sqrt(P)*ones(P,1); % Length scale for predictors sigmaF0 = 1; % Signal standard deviation
초기 잡음 표준편차를 1로 설정합니다.
sigmaN0 = 1;
상대 기울기 노름에 대한 종료 허용오차로 1e-2 를 지정합니다.
opts = statset('fitrgp');
opts.TolFun = 1e-2;초기 커널 모수 값, 초기 잡음 표준편차, 자동 관련성 결정(ARD) 제곱 지수 커널 함수를 사용하여 GPR 모델을 피팅합니다.
LBFGS 최적화 함수에 대한 초기 헤세 행렬 근사를 결정할 때 사용할 초기 스텝 크기를 1로 지정합니다.
gpr = fitrgp(X,y,'KernelFunction','ardsquaredexponential','Verbose',1, ... 'Optimizer','lbfgs','OptimizerOptions',opts, ... 'KernelParameters',[sigmaL0;sigmaF0],'Sigma',sigmaN0,'InitialStepSize',1);
o Parameter estimation: FitMethod = Exact, Optimizer = lbfgs
o Solver = LBFGS, HessianHistorySize = 15, LineSearchMethod = weakwolfe
|====================================================================================================|
| ITER | FUN VALUE | NORM GRAD | NORM STEP | CURV | GAMMA | ALPHA | ACCEPT |
|====================================================================================================|
| 0 | 3.004966e+02 | 2.569e+02 | 0.000e+00 | | 3.893e-03 | 0.000e+00 | YES |
| 1 | 9.525779e+01 | 1.281e+02 | 1.003e+00 | OK | 6.913e-03 | 1.000e+00 | YES |
| 2 | 3.972026e+01 | 1.647e+01 | 7.639e-01 | OK | 4.718e-03 | 5.000e-01 | YES |
| 3 | 3.893873e+01 | 1.073e+01 | 1.057e-01 | OK | 3.243e-03 | 1.000e+00 | YES |
| 4 | 3.859904e+01 | 5.659e+00 | 3.282e-02 | OK | 3.346e-03 | 1.000e+00 | YES |
| 5 | 3.748912e+01 | 1.030e+01 | 1.395e-01 | OK | 1.460e-03 | 1.000e+00 | YES |
| 6 | 2.028104e+01 | 1.380e+02 | 2.010e+00 | OK | 2.326e-03 | 1.000e+00 | YES |
| 7 | 2.001849e+01 | 1.510e+01 | 9.685e-01 | OK | 2.344e-03 | 1.000e+00 | YES |
| 8 | -7.706109e+00 | 8.340e+01 | 1.125e+00 | OK | 5.771e-04 | 1.000e+00 | YES |
| 9 | -1.786074e+01 | 2.323e+02 | 2.647e+00 | OK | 4.217e-03 | 1.250e-01 | YES |
| 10 | -4.058422e+01 | 1.972e+02 | 6.796e-01 | OK | 7.035e-03 | 1.000e+00 | YES |
| 11 | -7.850209e+01 | 4.432e+01 | 8.335e-01 | OK | 3.099e-03 | 1.000e+00 | YES |
| 12 | -1.312162e+02 | 3.334e+01 | 1.277e+00 | OK | 5.432e-02 | 1.000e+00 | YES |
| 13 | -2.005064e+02 | 9.519e+01 | 2.828e+00 | OK | 5.292e-03 | 1.000e+00 | YES |
| 14 | -2.070150e+02 | 1.898e+01 | 1.641e+00 | OK | 6.817e-03 | 1.000e+00 | YES |
| 15 | -2.108086e+02 | 3.793e+01 | 7.685e-01 | OK | 3.479e-03 | 1.000e+00 | YES |
| 16 | -2.122920e+02 | 7.057e+00 | 1.591e-01 | OK | 2.055e-03 | 1.000e+00 | YES |
| 17 | -2.125610e+02 | 4.337e+00 | 4.818e-02 | OK | 1.974e-03 | 1.000e+00 | YES |
| 18 | -2.130162e+02 | 1.178e+01 | 8.891e-02 | OK | 2.856e-03 | 1.000e+00 | YES |
| 19 | -2.139378e+02 | 1.933e+01 | 2.371e-01 | OK | 1.029e-02 | 1.000e+00 | YES |
|====================================================================================================|
| ITER | FUN VALUE | NORM GRAD | NORM STEP | CURV | GAMMA | ALPHA | ACCEPT |
|====================================================================================================|
| 20 | -2.151111e+02 | 1.550e+01 | 3.015e-01 | OK | 2.765e-02 | 1.000e+00 | YES |
| 21 | -2.173046e+02 | 5.856e+00 | 6.537e-01 | OK | 1.414e-02 | 1.000e+00 | YES |
| 22 | -2.201781e+02 | 8.918e+00 | 8.484e-01 | OK | 6.381e-03 | 1.000e+00 | YES |
| 23 | -2.288858e+02 | 4.846e+01 | 2.311e+00 | OK | 2.661e-03 | 1.000e+00 | YES |
| 24 | -2.392171e+02 | 1.190e+02 | 6.283e+00 | OK | 8.113e-03 | 1.000e+00 | YES |
| 25 | -2.511145e+02 | 1.008e+02 | 1.198e+00 | OK | 1.605e-02 | 1.000e+00 | YES |
| 26 | -2.742547e+02 | 2.207e+01 | 1.231e+00 | OK | 3.191e-03 | 1.000e+00 | YES |
| 27 | -2.849931e+02 | 5.067e+01 | 3.660e+00 | OK | 5.184e-03 | 1.000e+00 | YES |
| 28 | -2.899797e+02 | 2.068e+01 | 1.162e+00 | OK | 6.270e-03 | 1.000e+00 | YES |
| 29 | -2.916723e+02 | 1.816e+01 | 3.213e-01 | OK | 1.415e-02 | 1.000e+00 | YES |
| 30 | -2.947674e+02 | 6.965e+00 | 1.126e+00 | OK | 6.339e-03 | 1.000e+00 | YES |
| 31 | -2.962491e+02 | 1.349e+01 | 2.352e-01 | OK | 8.999e-03 | 1.000e+00 | YES |
| 32 | -3.004921e+02 | 1.586e+01 | 9.880e-01 | OK | 3.940e-02 | 1.000e+00 | YES |
| 33 | -3.118906e+02 | 1.889e+01 | 3.318e+00 | OK | 1.213e-01 | 1.000e+00 | YES |
| 34 | -3.189215e+02 | 7.086e+01 | 3.070e+00 | OK | 8.095e-03 | 1.000e+00 | YES |
| 35 | -3.245557e+02 | 4.366e+00 | 1.397e+00 | OK | 2.718e-03 | 1.000e+00 | YES |
| 36 | -3.254613e+02 | 3.751e+00 | 6.546e-01 | OK | 1.004e-02 | 1.000e+00 | YES |
| 37 | -3.262823e+02 | 4.011e+00 | 2.026e-01 | OK | 2.441e-02 | 1.000e+00 | YES |
| 38 | -3.325606e+02 | 1.773e+01 | 2.427e+00 | OK | 5.234e-02 | 1.000e+00 | YES |
| 39 | -3.350374e+02 | 1.201e+01 | 1.603e+00 | OK | 2.674e-02 | 1.000e+00 | YES |
|====================================================================================================|
| ITER | FUN VALUE | NORM GRAD | NORM STEP | CURV | GAMMA | ALPHA | ACCEPT |
|====================================================================================================|
| 40 | -3.379112e+02 | 5.280e+00 | 1.393e+00 | OK | 1.177e-02 | 1.000e+00 | YES |
| 41 | -3.389136e+02 | 3.061e+00 | 7.121e-01 | OK | 2.935e-02 | 1.000e+00 | YES |
| 42 | -3.401070e+02 | 4.094e+00 | 6.224e-01 | OK | 3.399e-02 | 1.000e+00 | YES |
| 43 | -3.436291e+02 | 8.833e+00 | 1.707e+00 | OK | 5.231e-02 | 1.000e+00 | YES |
| 44 | -3.456295e+02 | 5.891e+00 | 1.424e+00 | OK | 3.772e-02 | 1.000e+00 | YES |
| 45 | -3.460069e+02 | 1.126e+01 | 2.580e+00 | OK | 3.907e-02 | 1.000e+00 | YES |
| 46 | -3.481756e+02 | 1.546e+00 | 8.142e-01 | OK | 1.565e-02 | 1.000e+00 | YES |
Infinity norm of the final gradient = 1.546e+00
Two norm of the final step = 8.142e-01, TolX = 1.000e-12
Relative infinity norm of the final gradient = 6.016e-03, TolFun = 1.000e-02
EXIT: Local minimum found.
o Alpha estimation: PredictMethod = Exact
GPR 모델이 다수의 예측 변수를 갖는 ARD 커널을 사용하므로 헤세 행렬에 대한 LBFGS 근사를 사용하는 것이 전체 헤세 행렬을 저장하는 것보다 메모리 효율성이 더 높습니다. 또한, 초기 스텝 크기를 사용하여 초기 헤세 행렬 근삿값을 결정하면 최적화 속도를 높이는 데에도 도움이 될 수 있습니다.
음의 학습된 길이 스케일의 지수를 계산하여 예측 변수 가중치를 구합니다. 가중치를 정규화합니다.
sigmaL = gpr.KernelInformation.KernelParameters(1:end-1); % Learned length scales weights = exp(-sigmaL); % Predictor weights weights = weights/sum(weights); % Normalized predictor weights
정규화된 예측 변수 가중치를 플로팅합니다.
figure; semilogx(weights,'ro'); xlabel('Predictor index'); ylabel('Predictor weight');

훈련된 GPR 모델은 가장 큰 가중치를 4번째, 7번째, 13번째 예측 변수에 할당합니다. 관련 없는 예측 변수는 0에 가까운 가중치를 가집니다.
입력 인수
모델을 훈련시키는 데 사용되는 표본 데이터로, table로 지정됩니다. Tbl의 각 행은 하나의 관측값에 대응되고, 각 열은 하나의 변수에 대응됩니다. Tbl은 예측 변수를 포함하며, 선택적으로 응답 변수에 대한 하나의 열을 포함할 수도 있습니다. 문자형 벡터로 구성된 셀형 배열 이외의 셀형 배열과 다중 열 변수는 허용되지 않습니다.
Tbl이 응답 변수를 포함하며 나머지 모든 변수를 예측 변수로 사용하려는 경우ResponseVarName을 사용하여 응답 변수를 지정하십시오.Tbl이 응답 변수를 포함하며 모델을 훈련시킬 때 일부 예측 변수만 사용하려는 경우formula를 사용하여 응답 변수와 예측 변수를 지정하십시오.Tbl이 응답 변수를 포함하지 않는 경우y를 사용하여 응답 변수를 지정하십시오. 응답 변수의 길이와Tbl의 행 개수는 동일해야 합니다.
table 데이터형에 대한 자세한 내용은 table을 참조하십시오.
예측 변수 데이터에 범주형 변수가 포함된 경우 fitrgp는 가변수를 생성합니다. 자세한 내용은 CategoricalPredictors를 참조하십시오.
데이터형: table
응답 변수 이름으로, Tbl의 변수 이름으로 지정됩니다. ResponseVarName은 문자형 벡터나 string형 스칼라로 지정해야 합니다. 예를 들어, 응답 변수 y가 Tbl에 Tbl.y로 저장된 경우 이를 'y'로 지정하십시오. 이렇게 하지 않으면 모델을 훈련시킬 때 y를 포함한 Tbl의 모든 열이 예측 변수로 처리됩니다.
데이터형: char | string
모델 훈련에 사용할 응답 변수와 예측 변수로, 'y~x1+x2+x3' 형식의 문자형 벡터 또는 string형 스칼라로 지정됩니다. 이 형식에서 y는 응답 변수를 나타내고, x1, x2, x3은 모델 훈련에 사용할 예측 변수를 나타냅니다.
Tbl의 변수 중 일부를 모델 훈련에 사용할 예측 변수로 지정하려면 공식을 사용하십시오. 공식을 지정하면 formula에 표시되지 않는 변수는 모델 훈련에 사용되지 않습니다.
식에 포함되는 변수 이름은 Tbl에 포함된 변수 이름(Tbl.Properties.VariableNames)이면서 동시에 유효한 MATLAB® 식별자여야 합니다. isvarname 함수를 사용하여 Tbl에 포함된 변수 이름을 확인할 수 있습니다. 변수 이름이 유효하지 않으면 matlab.lang.makeValidName 함수를 사용하여 변수 이름을 변환할 수 있습니다.
공식은 BasisFunction 형식을 표시하지 않습니다.
예: 'PetalLength~PetalWidth+Species'는 변수 PetalLength를 응답 변수로 식별하고 PetalWidth 및 Species를 예측 변수로 식별합니다.
데이터형: char | string
GPR 모델의 예측 변수 데이터로, n×d 행렬로 지정됩니다. n은 관측값(행) 개수이고, d는 예측 변수(열) 개수입니다.
y의 길이와 X의 행 개수는 동일해야 합니다.
X에 나오는 순서로 예측 변수의 이름을 지정하려면 PredictorNames 이름-값 쌍의 인수를 사용하십시오.
데이터형: double
GPR 모델의 응답 변수 데이터로, n×1 벡터로 지정됩니다. y도 포함하는 Tbl 훈련 데이터를 지정하면 y는 생략할 수 있습니다. 이 경우, ResponseVarName을 사용하여 응답 변수를 식별하거나 formula를 사용하여 응답 변수와 예측 변수를 식별할 수 있습니다.
데이터형: double
이름-값 인수
선택적 인수 쌍을 Name1=Value1,...,NameN=ValueN으로 지정합니다. 여기서 Name은 인수 이름이고 Value는 대응값입니다. 이름-값 인수는 다른 인수 뒤에 와야 하지만, 인수 쌍의 순서는 상관없습니다.
R2021a 이전 릴리스에서는 쉼표를 사용하여 각 이름과 값을 구분하고 Name을 따옴표로 묶으십시오.
예: 'FitMethod','sr','BasisFunction','linear','ActiveSetMethod','sgma','PredictMethod','fic'는 모수 추정을 위해 부분 회귀 변수(subset of regressors) 근사법을 사용하여 GPR 모델을 훈련시키고, 선형 기저 함수를 사용하고, 활성 선택을 위해 희소 최대 일치(greedy) 행렬 근사를 사용하며, 예측에는 완전히 독립적인 조건부 근사법을 사용합니다.
참고
OptimizeHyperparameters 이름-값 인수는 어떠한 교차 검증 이름-값 인수와도 함께 사용할 수 없습니다. OptimizeHyperparameters에 대한 교차 검증을 수정하려면 HyperparameterOptimizationOptions 이름-값 인수를 사용해야만 합니다.
피팅
GPR 모델의 모수를 추정하는 방법으로, 다음 중 하나로 지정됩니다.
| 피팅 방법 | 설명 |
|---|---|
"none" | 추정 안 함. 초기 모수 값을 알려진 모수 값으로 사용합니다. |
"exact" | 정확한 가우스 과정 회귀. n ≤ 2000인 경우 이 값이 디폴트이며, 여기서 n은 관측값 개수입니다. |
"sd" | 부분 데이터 점 근사. n > 2000인 경우 이 값이 디폴트이며, 여기서 n은 관측값 개수입니다. "sd"는 희소 방법입니다. |
"sr" | 부분 회귀 변수 근사. "sr"은 희소 방법입니다. |
"fic" | 완전히 독립적인 조건부 근사. "fic"는 희소 방법입니다. |
예: FitMethod="fic"
GPR 모델의 명시적 기저로, "constant", "none", "linear", "pureQuadratic" 또는 함수 핸들로 지정됩니다. n이 관측값 개수이면 기저 함수는 항 H*β를 모델에 추가합니다. 여기서 H는 기저 행렬이고 β는 기저 계수로 구성된 p×1 벡터입니다.
| 명시적 기저 | 기저 행렬 |
|---|---|
"none" | 빈 행렬 |
"constant" |
H는 1로 구성된 n×1 벡터이며, 여기서 n은 관측값 개수입니다. |
"linear" |
X는 범주형 변수에 대해 가변수가 생성된 후의 확장된 예측 변수 데이터입니다. 가변수 생성에 대한 자세한 내용은 |
"pureQuadratic" |
여기서
이 기저 옵션에서는 범주형 예측 변수를 갖는 X가 지원되지 않습니다. |
| 함수 핸들 |
여기서 X는 예측 변수로 구성된 n×d 행렬이고, d는 범주형 변수에 대해 가변수가 생성된 후의 예측 변수 개수이고, H는 기저 함수로 구성된 n×p 행렬입니다. |
예: BasisFunction="pureQuadratic"
데이터형: char | string | function_handle
명시적 기저에 대한 계수의 초기값으로, p×1 벡터로 지정됩니다. 여기서 p는 기저 행렬 H의 열 개수입니다.
기저 행렬은 지정된 기저 함수에 따라 달라집니다. 자세한 내용은 BasisFunction 항목을 참조하십시오.
훈련 함수는 FitMethod가 "none"인 경우에만 알려진 계수 값으로 계수 초기값을 사용합니다.
데이터형: double
가우스 과정 모델의 잡음 표준편차에 대한 초기값으로, 양의 스칼라 값으로 지정됩니다.
훈련 함수는 잡음 표준편차를 SigmaLowerBound와 exp(η)의 합으로 모수화하며, 여기서 η는 비제약 값입니다. 따라서, Sigma가 작은 허용오차만큼 SigmaLowerBound보다 커야 함수가 η를 유한 값으로 초기화할 수 있습니다. 그렇지 않으면 함수가 Sigma를 호환되는 값으로 재설정합니다.
허용오차는 ConstantSigma가 false(디폴트 값)인 경우 1e-3이고 그렇지 않은 경우 1e-6입니다. 허용오차가 응답 변수의 스케일에 비해 충분히 작지 않은 경우, 허용오차 값이 응답 변수에 대해 작다고 간주될 수 있도록 응답 변수의 스케일을 크게 할 수 있습니다.
예: Sigma=2
데이터형: double
가우스 과정 모델의 잡음 표준편차의 Sigma 상수 값으로, 숫자형 또는 논리값 0(false)이나 1(true)로 지정됩니다. ConstantSigma가 true이면 훈련 함수는 Sigma의 값을 최적화하지 않고, 대신에 계산 전체 과정에서 초기값을 사용합니다.
예: ConstantSigma=true
데이터형: logical
잡음 표준편차(Sigma)의 하한으로, 양의 스칼라 값으로 지정됩니다.
Sigma는 작은 허용오차만큼 SigmaLowerBound보다 커야 합니다.
예: SigmaLowerBound=0.02
데이터형: double
범주형 예측 변수 목록으로, 다음 표에 있는 값 중 하나로 지정됩니다.
| 값 | 설명 |
|---|---|
| 양의 정수로 구성된 벡터 | 벡터의 각 요소는 대응되는 예측 변수가 범주형임을 나타내는 인덱스 값입니다. 인덱스 값은 1과
|
| 논리형 벡터 | 요소의 값이 |
| 문자형 행렬 | 행렬의 각 행은 예측 변수의 이름입니다. 이름은 PredictorNames의 요소와 일치해야 합니다. 문자형 행렬의 각 행의 길이가 같게 되도록 이름 뒤에 추가로 공백을 채웁니다. |
| string형 배열 또는 문자형 벡터로 구성된 셀형 배열 | 배열의 각 요소는 예측 변수의 이름입니다. 이름은 PredictorNames의 요소와 일치해야 합니다. |
"all" | 모든 예측 변수가 범주형 변수입니다. |
기본적으로 예측 변수 데이터가 테이블(Tbl) 내에 있는 경우, 변수가 논리형 벡터, categorical형 벡터, 문자형 배열, string형 배열 또는 문자형 벡터로 구성된 셀형 배열이면 fitrgp 함수는 그 변수를 범주형 변수라고 가정합니다. 예측 변수 데이터가 행렬(X)이면 fitrgp 함수는 모든 예측 변수를 연속형 변수라고 가정합니다. 다른 모든 예측 변수를 범주형 예측 변수로 식별하려면 이러한 변수를 CategoricalPredictors 이름-값 인수를 사용하여 지정하십시오.
식별된 범주형 예측 변수에 대해 fitrgp 함수는 범주형 변수에 순서가 지정되어 있는지에 따라 서로 다른 두 가지 체계를 사용하여 가변수를 생성합니다. 순서가 지정되지 않은 범주형 변수에 대해 fitrgp 함수는 범주형 변수의 각 수준마다 하나의 가변수를 생성합니다. 순서가 지정된 범주형 변수에 대해 fitrgp 함수는 범주 개수보다 하나가 적은 가변수를 생성합니다. 자세한 내용은 Automatic Creation of Dummy Variables 항목을 참조하십시오.
예: 'CategoricalPredictors','all'
데이터형: single | double | logical | char | string | cell
데이터 표준화 여부 표시자로, 숫자형 또는 논리값 0(false)이나 1(true)로 지정됩니다.
Standardize=1을 설정하면 예측 변수 데이터의 각 열이 열의 평균과 표준편차로 정규화됩니다. 범주형 예측 변수에 대해 생성된 가변수 열에 포함된 데이터는 표준화되지 않습니다.
예: Standardize=1
예: Standardize=true
데이터형: logical
부분 회귀 변수 근사법("sr")과 완전히 독립적인 조건부 근사법("fic")에 대한 정규화 표준편차로, 양의 스칼라 값으로 지정됩니다. 자세한 내용은 FitMethod 항목을 참조하십시오.
예: Regularization=0.2
데이터형: double
커널(공분산) 함수
공분산 함수의 형태로, 다음 중 하나로 지정됩니다.
| 값 | 설명 |
|---|---|
"exponential" | 지수 커널 |
"squaredexponential" | 제곱 지수 커널 |
"matern32" | 모수 3/2를 갖는 매턴 커널 |
"matern52" | 모수 5/2를 갖는 매턴 커널 |
"rationalquadratic" | 유리 2차 커널 |
"ardexponential" | 예측 변수당 개별적인 길이 스케일을 갖는 지수 커널 |
"ardsquaredexponential" | 예측 변수당 개별적인 길이 스케일을 갖는 제곱 지수 커널 |
"ardmatern32" | 모수 3/2 및 예측 변수당 개별적인 길이 스케일을 갖는 매턴 커널 |
"ardmatern52" | 모수 5/2 및 예측 변수당 개별적인 길이 스케일을 갖는 매턴 커널 |
"ardrationalquadratic" | 예측 변수당 개별적인 길이 스케일을 갖는 유리 2차 커널 |
| 함수 핸들 | 다음 형식의 함수 핸들:Kmn = kfcn(Xm,Xn,theta) . 여기서 Xm은 m×d 행렬이고, Xn은 n×d 행렬이고, Kmn은 커널 곱으로 구성된 m×n 행렬이며 이때 Kmn(i,j)는 Xm(i,:)와 Xn(j,:)의 커널 곱입니다. d는 범주형 변수에 대해 가변수가 생성된 후의 예측 변수 개수입니다. 가변수 생성에 대한 자세한 내용은 CategoricalPredictors 항목을 참조하십시오.theta는 kfcn에 대한 r×1 비제약 모수 벡터입니다. |
커널 함수에 대한 자세한 내용은 커널(공분산) 함수 옵션 항목을 참조하십시오.
예: KernelFunction="matern32"
데이터형: char | string | function_handle
커널 모수의 초기값으로, 숫자형 벡터로 지정됩니다. 벡터의 크기와 값은 KernelFunction 이름-값 인수로 지정되는 공분산 함수의 형태에 따라 달라집니다.
KernelFunction Value | KernelParameters Value |
|---|---|
"exponential", "squaredexponential", "matern32" 또는 "matern52" | 2×1 벡터 phi. 여기서 phi(1)은 길이 스케일을 포함하고 phi(2)는 신호 표준편차를 포함합니다. 길이 스케일 모수의 디폴트 초기값은 예측 변수의 표준편차 평균입니다. 신호 표준편차는 응답 변수의 표준편차를 2의 제곱근으로 나눈 값입니다. 즉, 다음과 같습니다. phi = [mean(std(X));std(y)/sqrt(2)] |
"rationalquadratic" | 3×1 벡터 phi. 여기서 phi(1)은 길이 스케일을 포함하고 phi(2)는 스케일 혼합 모수를 포함하며, phi(3)은 신호 표준편차를 포함합니다. 길이 스케일 모수의 디폴트 초기값은 예측 변수의 표준편차 평균입니다. 신호 표준편차는 응답 변수의 표준편차를 2의 제곱근으로 나눈 값입니다. 스케일 혼합 모수의 디폴트 초기값은 1입니다. 즉, 다음과 같습니다. phi = [mean(std(X));1;std(y)/sqrt(2)] |
"ardexponential", "ardsquaredexponential", "ardmatern32" 또는 "ardmatern52" | (d+1)×1 벡터 phi. 여기서 phi(i)는 예측 변수 i에 대한 길이 스케일을 포함하고, phi(d+1)은 신호 표준편차를 포함합니다. d는 범주형 변수에 대해 가변수가 생성된 후의 예측 변수 개수입니다. 가변수 생성에 대한 자세한 내용은 CategoricalPredictors를 참조하십시오. 길이 스케일 모수의 디폴트 초기값은 예측 변수의 표준편차입니다. 신호 표준편차는 응답 변수의 표준편차를 2의 제곱근으로 나눈 값입니다. 즉, 다음과 같습니다. phi = [std(X)';std(y)/sqrt(2)] |
"ardrationalquadratic" | (d+2)×1 벡터 phi. 여기서 phi(i)는 예측 변수 i에 대한 길이 스케일을 포함하고, phi(d+1)은 스케일 혼합 모수를 포함하며, phi(d+2)는 신호 표준편차를 포함합니다. d는 범주형 변수에 대해 가변수가 생성된 후의 예측 변수 개수입니다. 가변수 생성에 대한 자세한 내용은 CategoricalPredictors 항목을 참조하십시오.길이 스케일 모수의 디폴트 초기값은 예측 변수의 표준편차입니다. 신호 표준편차는 응답 변수의 표준편차를 2의 제곱근으로 나눈 값입니다. 스케일 혼합 모수의 디폴트 초기값은 1입니다. 즉, 다음과 같습니다. phi = [std(X)';1;std(y)/sqrt(2)] |
| 함수 핸들 | r×1 벡터로, 사용자 지정 커널 함수 kfcn에 대한 비제약 모수 벡터 phi의 초기값으로 사용됩니다. KernelFunction이 함수 핸들이면 커널 모수의 초기값을 지정해야 합니다. |
커널 함수에 대한 자세한 내용은 커널(공분산) 함수 옵션 항목을 참조하십시오.
예: KernelParameters=phi
데이터형: double | single
내장 커널 함수를 계산하기 위해 점 간 거리를 계산하는 방법으로, "fast" 또는 "accurate"로 지정됩니다. "fast"를 지정하면, 훈련 함수는 을 로 계산합니다. "accurate"를 지정하면, 훈련 함수는 을 계산합니다.
예: DistanceMethod="accurate"
활성 세트 선택
활성 세트 내 관측값으로, 1에서 n 사이의 정수로 구성된 m×1 벡터(m ≤ n) 또는 적어도 하나의 true 요소를 가지는 길이가 n인 논리형 벡터로 지정됩니다. n은 훈련 데이터에 포함된 총 관측값 개수입니다.
fitrgp는 ActiveSet에서 명시된 관측값을 사용해 GPR 모델을 훈련시킵니다. 활성 세트에는 중복된 요소가 있을 수 없습니다.
ActiveSet를 지정하는 경우,
fitrgp가ActiveSetSize및ActiveSetMethod를 사용하지 않습니다.이 모델에 대해 교차 검증을 수행할 수 없습니다.
데이터형: double | logical
활성 세트의 크기로, 1 ≤ m ≤ n을 충족하는 정수 m으로 지정됩니다. 여기서 n은 관측값 개수입니다. 이 인수는 FitMethod가 "sd", "sr" 또는 "fic"인 경우 유효합니다.
디폴트 값은 FitMethod가 "sr" 또는 "fic"인 경우 min(1000,n)이고, 그렇지 않은 경우 min(2000,n)입니다.
예: ActiveSetSize=100
데이터형: double
활성 세트 선택 방법으로, 다음 값 중 하나로 지정됩니다.
| 값 | 설명 |
|---|---|
"random" | 임의 선택 |
"sgma" | 희소 최대 일치(greedy) 행렬 근사 |
"entropy" | 미분 엔트로피에 기반한 선택 |
"likelihood" | 부분 회귀 변수 로그 가능도에 기반한 선택 |
("random"을 제외한) 모든 활성 세트 선택 방법은 n×m 행렬의 저장 공간을 필요로 합니다. 여기서 m은 활성 세트의 크기이고 n은 관측값 개수입니다.
예: ActiveSetMethod="entropy"
활성 세트 선택 시 최대 일치(greedy) 항목으로 포함될 수 있는 임의 탐색 세트 크기로, 정수 값으로 지정됩니다.
예: RandomSearchSetSize=30
데이터형: double
활성 세트 선택을 종료하기 위한 상대 허용오차로, 양의 스칼라로 지정됩니다.
예: ToleranceActiveset=0.0002
데이터형: double
ActiveSetMethod가 "random"이 아닌 경우 인터리빙된 활성 세트를 선택하고 모수를 추정할 때 수행할 반복 횟수로, 정수 값으로 지정됩니다.
예: NumActiveSetRepeats=5
데이터형: double
예측
모수가 주어진 경우 가우스 과정 모델에서 예측을 수행하는 데 사용되는 방법으로, 다음 값 중 하나로 지정됩니다.
| 값 | 설명 |
|---|---|
"exact" | 정확한 가우스 과정 회귀 방법. n ≤ 10,000인 경우 이 값이 디폴트입니다. |
"bcd" | 블록 좌표 하강법(BCD). n > 10,000인 경우 이 값이 디폴트입니다. |
"sd" | 부분 데이터 점 근사 |
"sr" | 부분 회귀 변수 근사 |
"fic" | 완전히 독립적인 조건부 근사 |
예: PredictMethod="bcd"
블록 좌표 하강법("bcd")의 블록 크기로, 1에서 n까지의 범위 내에 있는 정수로 지정됩니다. 여기서 n은 관측값 개수입니다.
예: BlockSizeBCD=1500
데이터형: double
블록 좌표 하강법("bcd")의 최대 일치(greedy) 선택 항목의 개수로, 1에서 BlockSizeBCD까지의 범위 내에 있는 정수로 지정됩니다.
예: NumGreedyBCD=150
데이터형: double
블록 좌표 하강법("bcd") 반복을 종료하는 데 사용되는 기울기 노름에 대한 상대 허용오차로, 양의 스칼라로 지정됩니다.
예: ToleranceBCD=0.002
데이터형: double
블록 좌표 하강법("bcd") 반복을 종료하는 데 사용되는 스텝 크기에 대한 절대 허용오차로, 양의 스칼라로 지정됩니다.
예: StepToleranceBCD=0.002
데이터형: double
블록 좌표 하강법("bcd") 반복의 최대 횟수로, 양의 정수로 지정됩니다.
예: IterationLimitBCD=10000
데이터형: double
최적화
모수 추정에 사용할 최적화 함수로, 다음 표에 나와 있는 값 중 하나로 지정됩니다.
| 값 | 설명 |
|---|---|
'quasinewton' | 헤세 행렬에 대한 조밀한 대칭 랭크 1 기반 준뉴턴 근사 |
'lbfgs' | 헤세 행렬에 대한 LBFGS 기반 준뉴턴 근사 |
'fminsearch' | 라가리아스(Lagarias) 등 [5]의 단체(Simplex) 탐색 방법을 사용한 제약 조건이 없는 비선형 최적화 |
'fminunc' | 제약 조건이 없는 비선형 최적화(Optimization Toolbox™ 라이선스 필요) |
'fmincon' | 제약 조건이 있는 비선형 최적화(Optimization Toolbox 라이선스 필요) |
최적화 함수에 대한 자세한 내용은 알고리즘 항목을 참조하십시오.
예: 'Optimizer','fmincon'
Optimizer 이름-값 인수로 설정하는 최적화 함수 옵션으로, optimset, statset("fitrgp") 또는 optimoptions로 생성되는 구조체 또는 객체로 지정됩니다.
| 최적화 함수 | 최적화 함수 옵션을 생성하는 함수 |
|---|---|
"fminsearch" | optimset(구조체) |
"quasinewton" 또는 "lbfgs" | statset("fitrgp")(구조체) |
"fminunc" 또는 "fmincon" | optimoptions(객체) |
디폴트 옵션은 지정된 최적화 함수에 따라 달라집니다.
예: OptimizerOptions=opt
초기 스텝 크기로, 양의 실수형 스칼라 또는 "auto"로 지정됩니다.
InitialStepSize는 최적화 함수가 "quasinewton" 또는 "lbfgs"인 경우 첫 번째 최적화 스텝의 근사 최대 절댓값입니다. 초기 스텝 크기를 통해 최적화 중에 초기 헤세 행렬에 대한 근삿값을 구할 수 있습니다.
기본적으로, 훈련 함수는 초기 스텝 크기를 사용하여 초기 헤세 행렬에 대한 근삿값을 구하지 않습니다. 초기 스텝 크기를 사용하려면, InitialStepSize 이름-값 인수 값을 설정하거나 자동으로 값을 구하도록 InitialStepSize="auto"를 지정하십시오. "auto"에 대한 자세한 내용은 알고리즘 항목을 참조하십시오.
예: InitialStepSize="auto"
교차 검증
교차 검증 여부 표시자로, 'off' 또는 'on'으로 지정됩니다. 'on'이면 fitrgp가 10겹 교차 검증된 GPR 모델을 반환합니다.
KFold, Holdout, Leaveout 또는 CVPartition 이름-값 쌍의 인수 중 하나를 사용하여 디폴트 교차 검증 설정을 변경할 수 있습니다. 이러한 이름-값 쌍의 인수는 한 번에 하나만 사용할 수 있습니다.
또는 모델에 crossval 방법을 사용할 수 있습니다.
예: 'CrossVal','on'
홀드아웃 검증에서 검정에 사용할 데이터의 비율로, (0,1) 범위 내에 있는 스칼라 값으로 지정됩니다. 'Holdout',p를 지정하면 소프트웨어가 다음 동작을 수행합니다.
1. 데이터의 p*100%를 무작위로 선택하여 검증 데이터용으로 남겨두고 나머지 데이터를 사용하여 모델을 훈련시킵니다.
2. 훈련된 간소 모델을 cvMdl.Trained에 저장합니다.
예: 'Holdout', 0.3은 검정에 데이터의 30%를 사용하고 훈련에 데이터의 70%를 사용합니다.
Holdout을 지정할 경우 CVPartition, KFold 또는 Leaveout을 지정할 수 없습니다.
데이터형: double
교차 검증된 GPR 모델에 사용할 겹의 개수로, 양의 정수 값으로 지정됩니다. KFold는 1보다 커야 합니다. 'KFold',k를 지정하면 소프트웨어가 다음 동작을 수행합니다.
1. 데이터를 k개 세트로 임의로 분할합니다.
2. 각 세트마다 해당 세트를 검정 데이터로 남겨두고 나머지 k – 1개의 세트를 사용하여 모델을 훈련시킵니다.
3. cvMdl.Trained의 k×1 셀형 배열의 셀에 k개의 훈련된 간소 모델을 저장합니다.
예: 'KFold',5는 교차 검증에 5겹을 사용합니다. 즉, 각각의 겹을 검정 데이터로 사용하고 나머지 4겹으로 모델을 훈련시킵니다.
KFold를 지정할 경우 CVPartition, Holdout 또는 Leaveout을 지정할 수 없습니다.
데이터형: double
리브-원-아웃 교차 검증 여부 표시자로, 'off' 또는 'on'으로 지정됩니다.
'Leaveout','on'을 지정하는 경우, n개 관측값 각각에 대해 소프트웨어가 다음 동작을 수행합니다.
1. 관측값을 검정 데이터로 남겨두고 나머지 n – 1개 관측값을 사용하여 모델을 훈련시킵니다.
2. n×1 셀형 배열 cvMdl.Trained의 셀에 훈련된 간소 모델을 저장합니다.
예: 'Leaveout','on'
Leaveout을 지정할 경우 CVPartition, Holdout 또는 KFold를 지정할 수 없습니다.
하이퍼파라미터 최적화
최적화할 모수로, 다음 값 중 하나로 지정됩니다.
'none'— 최적화하지 않습니다.'auto'—{'Sigma','Standardize'}를 사용합니다.'all'— 모든 적합한 모수를 최적화하며, 이는{'BasisFunction','KernelFunction','KernelScale','Sigma','Standardize'}와 동일합니다.적합한 모수 이름으로 구성된 string형 배열 또는 셀형 배열.
optimizableVariable객체로 구성된 벡터. 일반적으로hyperparameters의 출력값입니다.
최적화는 모수를 변경하여 fitrgp에 대한 교차 검증 손실(오차)을 최소화하려고 시도합니다. 교차 검증 유형과 최적화의 기타 측면을 제어하려면 HyperparameterOptimizationOptions 이름-값 인수를 사용하십시오. HyperparameterOptimizationOptions를 사용하는 경우, ConstraintType 옵션과 ConstraintBounds 옵션을 설정하여 교차 검증 손실 대신에 (간소) 모델 크기를 최적화 목적 함수로 사용할 수 있습니다.
참고
OptimizeHyperparameters 값은 다른 이름-값 인수를 사용하여 지정하는 모든 값을 재정의합니다. 예를 들어 OptimizeHyperparameters를 "auto"로 설정하면 fitrgp 함수는 "auto" 옵션에 대응되는 하이퍼파라미터를 최적화하고 하이퍼파라미터에 대해 지정된 값을 모두 무시합니다.
fitrgp에 대한 적합한 모수는 다음과 같습니다.
BasisFunction—fitrgp가'constant','none','linear','pureQuadratic'중에서 탐색을 수행합니다.KernelFunction—fitrgp가'ardexponential','ardmatern32','ardmatern52','ardrationalquadratic','ardsquaredexponential','exponential','matern32','matern52','rationalquadratic','squaredexponential'중에서 탐색을 수행합니다.KernelScale—fitrgp가KernelParameters인수를 사용하여 피팅 중에 일정하게 유지되는 커널 스케일 모수의 값을 지정합니다. 이 경우, 모든 입력 차원이 동일한KernelScale값을 갖도록 제한됩니다.fitrgp는 범위[1e-3,1e3]내에서 로그 스케일링된 양의 값을 대상으로 탐색을 수행합니다.KernelScale은 어떠한 ARD 커널에 대해서도 최적화될 수 없습니다.Sigma—fitrgp는 범위[1e-4,max(1e-3,10*ResponseStd)]내에서 로그 스케일링된 양의 값을 대상으로 탐색을 수행하며, 이 경우 다음과 같습니다.ResponseStd = std(y).내부적으로,
fitrgp는ConstantSigma이름-값 쌍을true로 설정하여Sigma의 값이 피팅 중에 일정하게 유지됩니다.Standardize—fitrgp가true및false중에서 탐색을 수행합니다.
디폴트가 아닌 값을 가지는 optimizableVariable 객체로 구성된 벡터를 전달하여 디폴트가 아닌 모수를 설정합니다. 예를 들면 다음과 같습니다.
load fisheriris params = hyperparameters('fitrgp',meas,species); params(1).Range = [1e-4,1e6];
params를 OptimizeHyperparameters의 값으로 전달합니다.
기본적으로, 반복 표시가 명령줄에 표시되고, 최적화에 지정된 하이퍼파라미터 개수에 따라 플롯이 표시됩니다. 최적화와 플롯에 대해 목적 함수는 log(1 + cross-validation loss)입니다. 반복 표시를 제어하려면 HyperparameterOptimizationOptions 이름-값 인수에 대한 Verbose 옵션을 설정하십시오. 플롯을 제어하려면 HyperparameterOptimizationOptions 이름-값 인수의 ShowPlots 옵션을 설정하십시오.
예제는 GPR 회귀 최적화하기 항목을 참조하십시오.
예: 'auto'
최적화에 사용할 옵션으로, HyperparameterOptimizationOptions 객체 또는 구조체로 지정됩니다. 이 인수는 OptimizeHyperparameters 이름-값 인수의 효과를 수정합니다. HyperparameterOptimizationOptions를 지정하는 경우 OptimizeHyperparameters도 지정해야 합니다. 모든 옵션은 선택 사항입니다. 그러나 AggregateOptimizationResults를 반환하려면 ConstraintBounds와 ConstraintType을 설정해야 합니다. 구조체에 설정할 수 있는 옵션은 HyperparameterOptimizationOptions 객체의 옵션과 동일합니다.
| 옵션 | 값 | 디폴트 값 |
|---|---|---|
Optimizer |
| "bayesopt" |
ConstraintBounds | N개의 최적화 문제에 대한 제약 조건 범위로, N×2 숫자형 행렬 또는 | [] |
ConstraintTarget | 최적화 문제에 대한 제약 조건 대상으로, | ConstraintBounds와 ConstraintType을 지정하면 디폴트 값은 "matlab"입니다. 그렇지 않은 경우 디폴트 값은 []입니다. |
ConstraintType | 최적화 문제애 대한 제약 조건 유형으로, | [] |
AcquisitionFunctionName | 획득 함수의 유형은 다음과 같습니다.
최적화는 목적 함수의 런타임에 종속적이기 때문에 이름에 | "expected-improvement-per-second-plus" |
MaxObjectiveEvaluations | 목적 함수 실행의 최대 횟수입니다. ConstraintBounds를 사용하여 여러 최적화 문제를 지정하는 경우 MaxObjectiveEvaluations의 값이 각 최적화 문제에 개별적으로 적용됩니다. | "bayesopt"와 "randomsearch"의 경우 30, "gridsearch"의 경우 전체 그리드 |
MaxTime | 최적화에 대한 시간 제한으로, 음이 아닌 실수형 스칼라로 지정됩니다. 시간 제한은 초 단위이며, | Inf |
NumGridDivisions | Optimizer="gridsearch"의 경우, 각 차원의 값 개수입니다. 이 값은 각 차원에 대한 값의 개수를 제공하는 양의 정수로 구성된 벡터 또는 모든 차원에 적용되는 스칼라일 수 있습니다. 이 옵션은 범주형 변수의 경우 무시됩니다. | 10 |
ShowPlots | 최적화 진행률의 플롯 표시 여부를 나타내는 논리값입니다. 이 옵션이 true이면 반복 횟수에 대해 최선의 관측된 목적 함수 값이 플로팅됩니다. 베이즈 최적화(Optimizer="bayesopt")를 사용하는 경우에는 최선의 추정된 목적 함수 값도 플로팅됩니다. 최선의 관측된 목적 함수 값과 최선의 추정된 목적 함수 값은 각각 반복 표시의 BestSoFar (observed) 열과 BestSoFar (estim.) 열의 값에 대응됩니다. Mdl.HyperparameterOptimizationResults의 속성 ObjectiveMinimumTrace 및 EstimatedObjectiveMinimumTrace에서 이러한 값을 확인할 수 있습니다. 문제에 베이즈 최적화를 위한 하나 또는 두 개의 최적화 모수가 있는 경우, ShowPlots는 이 모수에 대해서도 목적 함수의 모델을 플로팅합니다. | true |
SaveIntermediateResults | 최적화 결과를 저장할지 여부를 나타내는 논리값입니다. 이 옵션이 true이면 각 반복마다 "BayesoptResults"라는 이름의 작업 공간 변수를 덮어쓰게 됩니다. 변수는 BayesianOptimization 객체입니다. ConstraintBounds를 사용하여 여러 최적화 문제를 지정하는 경우, 작업 공간 변수는 "AggregateBayesoptResults"라는 이름의 AggregateBayesianOptimization 객체입니다. | false |
Verbose | 명령줄에서 표시 수준은 다음과 같습니다.
자세한 내용은 | 1 |
UseParallel | 베이즈 최적화를 병렬로 실행할지 여부를 나타내는 논리값으로, Parallel Computing Toolbox™가 필요합니다. 병렬 시간 재현이 불가능하기 때문에, 병렬 베이즈 최적화에서 반드시 재현 가능한 결과를 산출하지는 않습니다. 자세한 내용은 Parallel Bayesian Optimization 항목을 참조하십시오. | false |
Repartition | 매 반복 시 교차 검증을 다시 분할할지 여부를 나타내는 논리값입니다. 이 옵션이 값이 | false |
| 다음 3가지 옵션 중 하나만 지정합니다. | ||
CVPartition | cvpartition으로 생성된 cvpartition 객체 | 교차 검증 옵션을 지정하지 않는 경우 KFold=5 |
Holdout | 홀드아웃 비율을 나타내는 범위 (0,1) 내에 있는 스칼라 | |
KFold | 1보다 큰 정수 | |
예: HyperparameterOptimizationOptions=struct(UseParallel=true)
기타
예측 변수 이름으로, 고유한 이름으로 구성된 string형 배열 또는 고유한 문자형 벡터로 구성된 셀형 배열로 지정됩니다. 'PredictorNames'의 기능은 훈련 데이터를 어떤 방식으로 제공하느냐에 따라 달라집니다.
X와y를 제공하는 경우,'PredictorNames'를 사용하여X이름에 예측 변수를 제공할 수 있습니다.PredictorNames의 이름의 순서는X의 열 순서와 일치해야 합니다. 즉,PredictorNames{1}은X(:,1)의 이름이고,PredictorNames{2}는X(:,2)의 이름이 되는 식입니다. 또한,size(X,2)와numel(PredictorNames)는 같아야 합니다.기본적으로
PredictorNames는{'x1','x2',...}입니다.
Tbl을 제공하는 경우,'PredictorNames'를 사용하여 훈련에 사용할 예측 변수를 선택할 수 있습니다. 즉,fitrgp함수는PredictorNames의 예측 변수와 이에 대한 응답 변수만을 훈련에 사용합니다.PredictorNames는Tbl.Properties.VariableNames의 부분 집합이어야 하므로 응답 변수의 이름은 포함할 수 없습니다.기본적으로,
PredictorNames는 모든 예측 변수의 이름을 포함합니다.'PredictorNames'또는formula중 하나만 사용하여 훈련에 사용할 예측 변수를 지정하는 것이 좋습니다.
예: 'PredictorNames',{'PedalLength','PedalWidth'}
데이터형: string | cell
응답 변수 이름으로, 문자형 벡터 또는 string형 스칼라로 지정됩니다.
Y를 제공하는 경우,ResponseName을 사용하여 응답 변수의 이름을 지정할 수 있습니다.ResponseVarName또는formula를 제공하는 경우에는ResponseName을 사용할 수 없습니다.
예: ResponseName="response"
데이터형: char | string
세부 정보 표시 수준으로, 0 또는 1로 지정됩니다.
0— 훈련 함수는 활성 세트 선택 및 블록 좌표 하강법과 관련된 진단 메시지를 표시하지 않지만OptimizerOptions의Display값에 따라 모수 추정과 관련된 메시지를 표시합니다.1— 훈련 함수는 모수 추정, 활성 세트 선택, 블록 좌표 하강법과 관련된 반복 진단 메시지를 표시합니다.
예: Verbose=1
메가바이트(MB) 단위의 캐시 크기로, 양의 스칼라로 지정됩니다. 캐시 크기는 피팅과 활성 세트 선택에 필요한 메모리 외에 사용 가능한 여분의 메모리입니다. 훈련 함수는 CacheSize를 사용하여 다음을 수행합니다.
모수를 추정할 때 점 간 거리를 캐시할지 여부를 결정합니다.
블록 좌표 하강법과 예측 수행을 위해 행렬 벡터 곱이 계산되는 방법을 결정합니다.
예: CacheSize=2000
데이터형: double
출력 인수
가우스 과정 회귀 모델로, RegressionGP 모델 객체 또는 RegressionPartitionedGP 모델 객체로 반환됩니다. OptimizeHyperparameters를 지정하고 HyperparameterOptimizationOptions의 ConstraintType 옵션과 ConstraintBounds 옵션을 설정하면 Mdl은 모델 객체로 구성된 N×1 셀형 배열입니다. 여기서 N은 ConstraintBounds의 행 개수와 동일합니다. 최적화 문제 중 어느 것도 실현가능 모델을 산출하지 못하면 각 셀형 배열 값은 []입니다.
교차 검증을 수행하는 경우, 즉
'Crossval','KFold','Holdout','Leaveout'또는'CVPartition'이름-값 인수 중 하나를 사용하는 경우Mdl은RegressionPartitionedGP모델 객체입니다.kfoldPredict를 사용하여fitrgp가 훈련하는 동안 홀드아웃한 관측값에 대한 응답 변수를 예측할 수 있습니다.kfoldPredict는 해당 관측값 없이 훈련된 모델을 사용하여 각 관측값에 대한 응답 변수를 예측합니다. 교차 검증된 모델에 대해서는 예측 구간을 계산할 수 없습니다.교차 검증을 수행하지 않는 경우
Mdl은RegressionGP모델 객체입니다.predict를 사용하여 새 관측값에 대한 응답 변수를 예측하고resubPredict를 사용하여 훈련 관측값에 대한 응답 변수를 예측할 수 있습니다.predict및resubPredict를 사용하여 예측 구간을 계산할 수도 있습니다.
여러 최적화 문제에 대한 최적화 결과 집계로, AggregateBayesianOptimization 객체로 반환됩니다. AggregateOptimizationResults를 반환하려면 OptimizeHyperparameters와 HyperparameterOptimizationOptions를 지정해야 합니다. HyperparameterOptimizationOptions의 ConstraintType 옵션과 ConstraintBounds 옵션도 지정해야 합니다. 이 출력값을 생성하는 방법을 보여주는 예제는 Hyperparameter Optimization with Multiple Constraint Bounds 항목을 참조하십시오.
세부 정보
부분 데이터 근사, 부분 회귀 변수 근사 또는 완전히 독립적인 조건부 근사 피팅 방법(FitMethod가 'sd', 'sr' 또는 'fic'임)의 경우, 활성 세트(또는 유도 입력 세트)를 지정하지 않으면 fitrgp가 일련의 반복에서 활성 세트를 선택하고 모수 추정값을 계산합니다.
첫 번째 반복에서 소프트웨어는 벡터 η0 = [β0,σ0,θ0]의 초기 모수 값을 사용하여 활성 세트 A1을 선택합니다. η0을 초기값으로 사용하고 A1을 사용하여 GPR 주변 로그 가능도 또는 해당 근삿값을 최대화하여 새 모수 추정값 η1을 계산합니다. 그런 다음, η1과 A1을 사용하여 새 로그 가능도 L1을 계산합니다.
두 번째 반복에서 소프트웨어는 η1의 모수 값을 사용하여 활성 세트 A2를 선택합니다. 그런 다음, η1을 초기값으로 사용하고 A2를 사용하여 GPR 주변 로그 가능도 또는 해당 근삿값을 최대화하고 새 모수 값 η2를 추정합니다. 다음으로, η2와 A2를 사용하여 새 로그 가능도 값 L2를 계산합니다.
다음 표에는 각 반복과 해당 반복에서의 계산이 요약되어 있습니다.
| 반복 횟수 | 활성 세트 | 모수 벡터 | 로그 가능도 |
|---|---|---|---|
| 1 | A1 | η1 | L1 |
| 2 | A2 | η2 | L2 |
| 3 | A3 | η3 | L3 |
| … | … | … | … |
지정된 반복 횟수 동안 유사하게 반복이 수행됩니다. NumActiveSetRepeats 이름-값 인수를 사용하여 활성 세트 선택 시 수행할 반복 실험 수를 지정할 수 있습니다.
팁
fitrgp는 피팅, 예측, 활성 세트 선택 방법의 모든 조합을 허용합니다. 예측된 응답의 표준편차를 계산할 수 없고 이로 인해 예측 구간 역시 계산할 수 없는 경우가 있을 수 있습니다.predict를 참조하십시오. 또한, 경우에 따라 정확한 방법을 사용하면 훈련 데이터의 크기로 인해 시간이 오래 걸릴 수 있습니다.PredictorNames속성은 원래 예측 변수 이름마다 하나의 요소를 저장합니다. 예를 들어, 예측 변수가 3개 있고 그중 하나가 3개 수준을 갖는 범주형 변수인 경우PredictorNames는 문자형 벡터로 구성된 1×3 셀형 배열입니다.ExpandedPredictorNames속성은 가변수를 포함하여 예측 변수마다 하나의 요소를 저장합니다. 예를 들어, 예측 변수가 3개 있고 그중 하나가 3개 수준을 갖는 범주형 변수인 경우ExpandedPredictorNames는 문자형 벡터로 구성된 1×5 셀형 배열입니다.마찬가지로,
Beta속성은 가변수를 포함하여 예측 변수마다 하나의 베타 계수를 저장합니다.X속성은 훈련 데이터를 원래 입력된 대로 저장합니다. 가변수는 포함하지 않습니다.fitrgp에서 헤세 행렬 근삿값을 초기화하는 기본 접근법은 다수의 예측 변수를 갖는 ARD 커널을 사용하는 경우와 같이 다수의 커널 모수를 갖는 GPR 모델이 있는 경우 느릴 수 있습니다. 이 경우,'auto'또는 초기 스텝 크기의 값을 지정하는 것이 좋습니다.반복 진단 메시지를 표시하려면
'Verbose',1을 선택하고 디폴트fitrgp최적화로 LBFGS 또는 준뉴턴 최적화 함수를 사용하여 GPR 모델 훈련을 시작할 수 있습니다. 몇 초 후 반복 진단 메시지가 표시되지 않으면 헤세 행렬 근삿값을 초기화하는 데 너무 많은 시간이 걸리는 것일 수 있습니다. 이 경우, 훈련을 다시 시작하고 초기 스텝 크기를 사용하여 최적화 속도를 높여 보십시오.모델을 훈련시킨 후에는 새 데이터에 대한 응답 변수를 예측하는 C/C++ 코드를 생성할 수 있습니다. C/C++ 코드를 생성하려면 MATLAB Coder™가 필요합니다. 자세한 내용은 Introduction to Code Generation for Statistics and Machine Learning Functions 항목을 참조하십시오. .
알고리즘
GPR 모델 피팅 과정에는 데이터에서 다음과 같은 모델 모수를 추정하는 작업이 포함됩니다.
벡터 의 커널 모수로 모수화되는 공분산 함수 (커널(공분산) 함수 옵션 참조)
잡음 분산
고정된 기저 함수의 계수 벡터
KernelParameters이름-값 인수의 값은 신호 표준편차 와 특성 길이 스케일 에 대한 초기값으로 구성된 벡터입니다. 이 값을 사용하여 커널 모수가 결정됩니다. 이와 유사하게Sigma이름-값 인수는 잡음 표준편차 에 대한 초기값을 포함합니다.최적화하는 동안 잡음 표준편차와 커널 모수에 대한 초기값을 사용하여 비제약 초기 모수 값 으로 구성된 벡터가 생성됩니다.
와 에 대한 추정된 값에서
Beta이름-값 인수로 지정된 명시적 기저 계수 가 해석적으로 판별됩니다. 따라서 수치 최적화를 초기화할 때 는 벡터에 나타나지 않습니다.참고
GPR 모델에 대한 모수의 추정값을 지정하지 않을 경우
Beta이름-값 인수 값과 기타 초기 모수 값이 알려진 GPR 모수 값으로 사용됩니다(Beta참조). 그 외 모든 경우,Beta값은 목적 함수에서 해석적으로 최적화됩니다.준뉴턴 최적화 함수는 헤세 행렬에 대한 조밀한 대칭 랭크 1 기반(SR1) 준뉴턴 근사와 함께 trust-region 방법을 사용합니다. LBFGS 최적화 함수는 헤세 행렬에 대한 LBFGS(limited-memory Broyden-Fletcher-Goldfarb-Shanno) 준뉴턴 근사와 함께 표준 직선 탐색 방법을 사용합니다. Nocedal과 Wright의 문헌 [6]을 참조하십시오.
InitialStepSize이름-값 인수를"auto"로 설정하는 경우 을 사용하여 초기 스텝 크기 가 결정됩니다.은 초기 스텝 벡터이고 은 비제약 초기 모수 값으로 구성된 벡터입니다.
최적화하는 동안 다음과 같이 초기 스텝 크기 가 사용됩니다.
초기 스텝 크기와 함께
Optimizer="quasinewton"을 지정하는 경우 초기 헤세 행렬 근삿값은 입니다.초기 스텝 크기와 함께
Optimizer="lbfgs"를 지정하는 경우 초기 역헤세 행렬 근삿값은 입니다.은 초기 기울기 벡터이고 는 단위 행렬입니다.
참고 문헌
[1] Nash, W.J., T. L. Sellers, S. R. Talbot, A. J. Cawthorn, and W. B. Ford. "The Population Biology of Abalone (Haliotis species) in Tasmania. I. Blacklip Abalone (H. rubra) from the North Coast and Islands of Bass Strait." Sea Fisheries Division, Technical Report No. 48, 1994.
[2] Waugh, S. "Extending and Benchmarking Cascade-Correlation: Extensions to the Cascade-Correlation Architecture and Benchmarking of Feed-forward Supervised Artificial Neural Networks." University of Tasmania Department of Computer Science thesis, 1995.
[3] Lichman, M. UCI Machine Learning Repository, Irvine, CA: University of California, School of Information and Computer Science, 2013. http://archive.ics.uci.edu/ml.
[4] Rasmussen, C. E. and C. K. I. Williams. Gaussian Processes for Machine Learning. MIT Press. Cambridge, Massachusetts, 2006.
[5] Lagarias, J. C., J. A. Reeds, M. H. Wright, and P. E. Wright. "Convergence Properties of the Nelder-Mead Simplex Method in Low Dimensions." SIAM Journal of Optimization. Vol. 9, Number 1, 1998, pp. 112–147.
[6] Nocedal, J. and S. J. Wright. Numerical Optimization, Second Edition. Springer Series in Operations Research, Springer Verlag, 2006.
확장 기능
병렬 하이퍼파라미터 최적화를 수행하려면 fitrgp 함수에 대한 호출에 HyperparameterOptimizationOptions 이름-값 인수의 UseParallel=true 옵션을 사용하십시오.
병렬 하이퍼파라미터 최적화에 대한 자세한 내용은 Parallel Bayesian Optimization 항목을 참조하십시오.
병렬 연산에 대한 일반적인 내용은 자동 병렬 연산을 지원하는 MATLAB 함수 실행하기 (Parallel Computing Toolbox) 항목을 참조하십시오.
버전 내역
R2015b에 개발됨fitrgp 함수는 HyperparameterOptimizationOptions가 UseParallel=true를 포함하고 소프트웨어가 병렬 풀을 열 수 없으면 순차적 하이퍼파라미터 최적화를 디폴트 값으로 지정합니다.
이전 릴리스에서는 이러한 상황에서 소프트웨어가 오류를 발생시킵니다.
R2023b부터, OptimizeHyperparameters 값을 "auto"로 지정하면 fitrgp 함수는 Standardize를 최적화 가능한 하이퍼파라미터로 포함합니다.
R2023b부터, fitrgp 함수가 디폴트 탐색 범위 [1e-3,1e3]을 사용하여 가우스 과정 회귀(GPR) 모델의 커널 스케일 모수를 최적화합니다. 즉, OptimizeHyperparameters 이름-값 인수를 사용하여 GPR 하이퍼파라미터 KernelScale을 최적화하도록 지정하면 함수는 범위 [1e-3,1e3] 내에서 로그 스케일링된 양수 값들을 탐색합니다.
이전 릴리스에서 KernelScale 하이퍼파라미터의 디폴트 탐색 범위는 [1e-3*MaxPredictorRange,MaxPredictorRange]였으며, 이때 MaxPredictorRange = max(max(X) - min(X))입니다.
R2022b부터, 교차 검증된 가우스 과정 회귀(GPR) 모델은 RegressionPartitionedGP 객체입니다. 이전 릴리스에서 교차 검증된 GPR 모델은 RegressionPartitionedModel 객체였습니다.
다음 두 가지 방법으로 RegressionPartitionedGP 객체를 생성할 수 있습니다.
crossval객체 함수를 사용하여 GPR 모델 객체RegressionGP에서 교차 검증된 모델을 만듭니다.fitrgp함수를 사용하고 이름-값 인수CrossVal,CVPartition,Holdout,KFold또는Leaveout중 하나를 지정하여 교차 검증된 모델을 만듭니다.
전체 또는 교차 검증된 GPR 모델을 먼저 훈련시키든 상관없이 fitrgp에 대한 호출에서 ActiveSet 값을 지정할 수 없습니다.
MATLAB Command
You clicked a link that corresponds to this MATLAB command:
Run the command by entering it in the MATLAB Command Window. Web browsers do not support MATLAB commands.
웹사이트 선택
번역된 콘텐츠를 보고 지역별 이벤트와 혜택을 살펴보려면 웹사이트를 선택하십시오. 현재 계신 지역에 따라 다음 웹사이트를 권장합니다:
또한 다음 목록에서 웹사이트를 선택하실 수도 있습니다.
사이트 성능 최적화 방법
최고의 사이트 성능을 위해 중국 사이트(중국어 또는 영어)를 선택하십시오. 현재 계신 지역에서는 다른 국가의 MathWorks 사이트 방문이 최적화되지 않았습니다.
미주
- América Latina (Español)
- Canada (English)
- United States (English)
유럽
- Belgium (English)
- Denmark (English)
- Deutschland (Deutsch)
- España (Español)
- Finland (English)
- France (Français)
- Ireland (English)
- Italia (Italiano)
- Luxembourg (English)
- Netherlands (English)
- Norway (English)
- Österreich (Deutsch)
- Portugal (English)
- Sweden (English)
- Switzerland
- United Kingdom (English)